La forte variabilité au niveau individuel des précipitations du virus SARS-CoV-2 peut expliquer la prévalence élevée

Des chercheurs aux États-Unis ont fourni une description à haute résolution de la dynamique virale associée à une infection grave par le syndrome respiratoire aigu sévère 2 (SRAS-CoV-2) – l’agent qui cause la maladie à coronavirus 2019 (COVID-19).
L’échantillonnage longitudinal quotidien de l’équipe sur 60 personnes nouvellement infectées a révélé qu’une variation significative de personne à personne dans la libération de virus infectieux contribue à la propagation.
Généralisé est le terme utilisé pour décrire une petite partie des individus infectés représentant un niveau disproportionné de transmission communautaire.
« Ces résultats fournissent le premier profil expérimental multiparamétrique à haute résolution d’une infection sévère par le SRAS-CoV-2 chez l’homme et impliquent une variabilité de personne à personne dans la libération de virus infectieux dans les schémas de propagation épidémiologique de l’épidémie », a déclaré Christopher. a écrit. Brooke de l’Université de l’Illinois à Urbana-Champaign et ses collègues.
Une copie papier du document de recherche est disponible sur medRxiv* Serveur, tandis que l’article est soumis à un examen de miction.
La dynamique du SARS-CoV-2 est mal comprise
« Plusieurs explications comportementales et environnementales ont été avancées pour expliquer l’hétérogénéité de la transmission, mais la mesure dans laquelle les caractéristiques essentielles du processus d’infection au sein d’un seul hôte contribuent au phénomène de transmission généralisée reste incertaine », déclarent Brooke et son équipe.
Les chercheurs affirment que combler cette lacune dans les connaissances aidera à concevoir des stratégies plus ciblées et plus efficaces pour contrôler la propagation communautaire.
Qu’ont fait les chercheurs ?
L’équipe a effectué un échantillonnage longitudinal quotidien de 60 personnes infectées par le SRAS-CoV-2 pendant 14 jours pour capturer la dynamique de l’excrétion du virus infectieux et de l’ARN viral lors d’une infection aiguë.
En ajustant les modèles mécaniques, l’équipe a directement estimé la réplication virale, la désinfection et l’infection de chaque individu.
À l’automne 2020 et au printemps 2021, tous les professeurs, le personnel et les étudiants de l’Université de l’Illinois à Urbana-Champaign ont subi au moins deux fois une réaction en chaîne par polymérase quantitative par transcriptase inverse (RT-qPCR) pour le SRAS-CoV-2. UNE Semaine.
Brock et ses collègues ont profité de ce dépistage à grande échelle d’individus infectés (âge médian de 28 ans ; tranche d’âge de 19 à 73 ans) et ont testé des échantillons nasaux et salivaires quotidiens pour créer une image haute résolution de la dynamique virale au cours du stade précoce de infection.
Qu’ont-ils trouvé ?
Les résultats ont révélé un niveau élevé de variabilité d’une personne à l’autre dans l’élimination du virus infectieux, ce qui, selon l’équipe, fournit une explication partielle du rôle que jouent les super-épandeurs dans la transmission du SRAS-CoV-2 dans la communauté.
L’étude a révélé des différences statistiquement significatives au niveau individuel dans la durée de libération du virus infectieux, la cinétique de filtrage et la relation temporelle entre les sécrétions nasales et la salive.
Lorsque les chercheurs ont comparé les fréquences de symptômes signalées pour les jours où les individus ont été testés positifs ou négatifs pour l’infection, les douleurs musculaires, l’écoulement nasal et les irritations de la gorge étaient significativement plus susceptibles de rapporter les jours où les participants ont été testés positifs.
Cela suggère que ces symptômes spécifiques pourraient servir d’indicateurs potentiels d’une maladie infectieuse, selon les chercheurs.
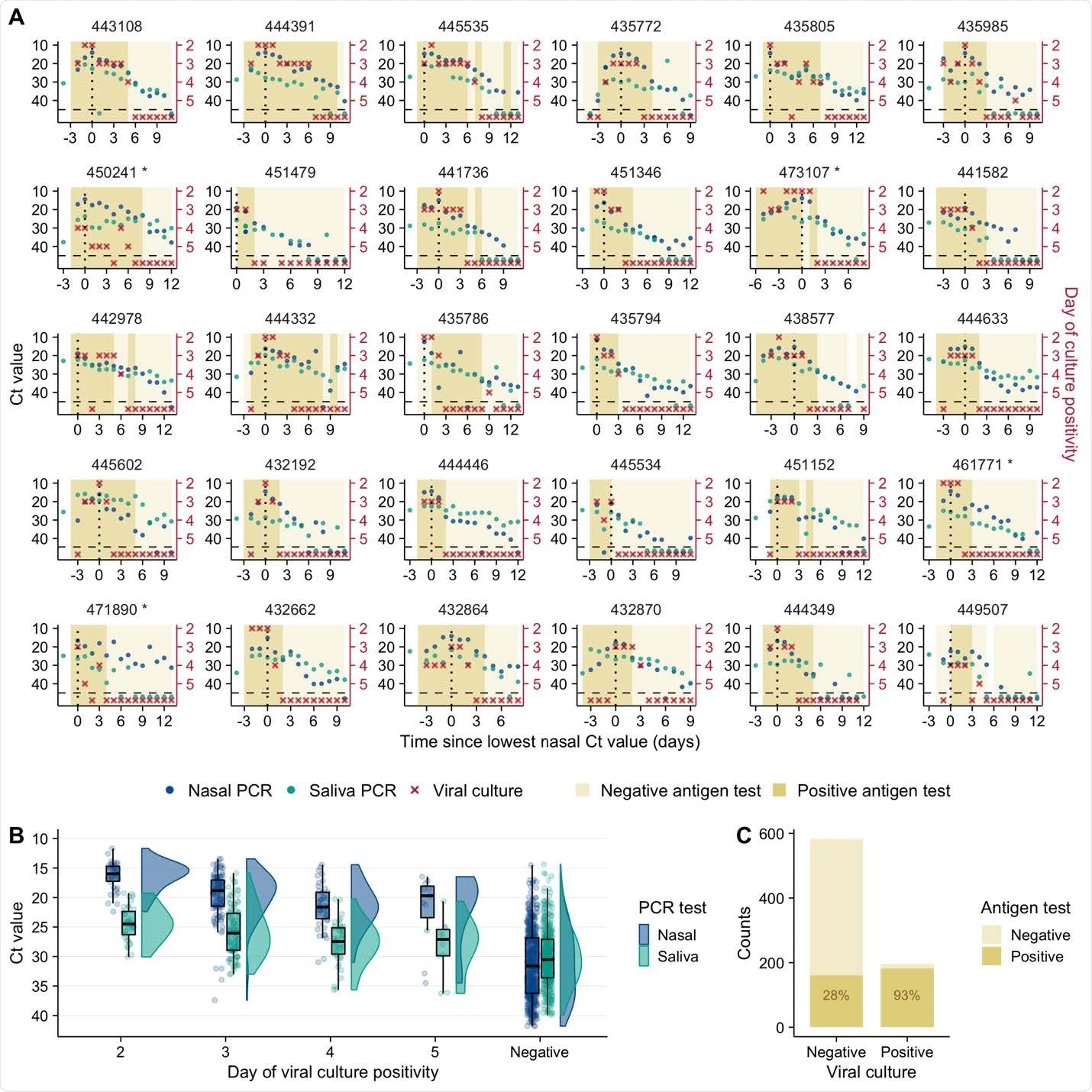
La séparation des génomes viraux a culminé plus tôt dans les échantillons de salive
Brooke et ses collègues ont observé un degré surprenant de divergence dans la dynamique virale entre les échantillons nasaux et de salive chez la plupart des participants.
Parmi 41 des 54 individus analysés, l’excrétion du génome viral a culminé au moins 1 jour plus tôt dans les échantillons de salive que dans les échantillons nasaux.
L’équipe dit que cela indique un fort clivage dans les cavités nasale et buccale et suggère que la salive pourrait servir d’excellent site d’échantillonnage pour la détection précoce de l’infection.
De plus, la clairance virale différait significativement entre les échantillons nasaux et salivaires, la charge du génome viral post-pic diminuant plus rapidement dans les échantillons nasaux que dans les échantillons de salive.
L’infection au niveau individuel était également très variable, avec une différence de plus de 30 fois entre le taux d’infection le plus élevé et le plus faible.
« Cela souligne le potentiel pour un petit sous-ensemble d’individus présentant une infection intrinsèque élevée d’agir comme » superprévalent « s’ils ont des contacts fréquents et/ou à haut risque au cours de l’infection », ont écrit les chercheurs.
Comparaison de la souche Alpha et des virus 1.17 autres que B.1.17
Les chercheurs ont comparé la dynamique d’élimination entre la variante B.1.1.7 (alpha) du SRAS-CoV-2 et les virus non-B.1.1.7 pour vérifier si des différences significatives d’élimination pourraient expliquer l’amélioration de la transmissibilité de B.1.1.7 .
L’analyse de 15 personnes infectées par B.1.1.7 a suggéré que la dynamique de libération du génome viral dans les échantillons nasaux ne pouvait pas être distinguée entre les infections à B.1.1.7 et non B.1.1.7 et qu’il n’y avait pas de différence significative dans l’ensemble infection entre les virus B. 1.1.7 et non B. B.1.1.7.
Cependant, l’analyse des échantillons de salive a montré une augmentation plus lente des charges virales avant le pic pour B.1.1.7, par rapport aux virus non-B.1.1.7.
L’équipe suggère: « Parce que l’apparition des symptômes semble se produire au moment du pic de charge virale, l’excrétion prolongée de la salive avant le pic par B.1.1.7 pourrait améliorer la transmissibilité en prolongeant la clairance virale présymptomatique. » « Cependant, davantage de données sont nécessaires pour déterminer s’il existe une association mécaniste entre la cinétique pic par pic et le potentiel de transmission. »
Qu’ont conclu les auteurs ?
Brooke et ses collègues disent que les résultats de ces échantillonnages multisectionnels quotidiens de la dynamique virale parmi des dizaines d’individus nouvellement infectés par le SRAS-CoV-2 fournissent la description la plus complète et la plus haute résolution de la dynamique de l’élimination et de l’élimination du SRAS-CoV-2 chez l’homme. . Date.
Dans l’ensemble, nos données fournissent une vue sans précédent de la dynamique virale longitudinale de l’infection par le SRAS-CoV-2 chez l’homme, impliquant à la fois une hétérogénéité au niveau individuel dans l’excrétion du virus et le compartiment oral et jouant un rôle essentiel dans la transmission.
*Remarque importante
medRxiv Il publie des rapports scientifiques préliminaires qui n’ont pas été évalués par des pairs et ne doivent donc pas être considérés comme concluants, guider la pratique clinique/le comportement lié à la santé ou être traités comme des informations établies.